Tri de lignées incomplet
Le tri de lignées incomplet[1],[2],[3],[4] (incomplete lineage sorting, ILS), aussi traduit comme tri de lignage incomplet (en abréviation TLI), décrit un phénomène en génétique des populations où des allèles différents coexistent dans la population de l’espèce ancestrale, puis sont fixés de manière différentielle dans les populations des espèces qui en descendent.
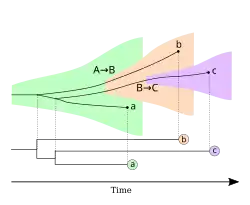
Par exemple dans l'espèce A le gène G mute pour donner d'abord l'allèle Gh puis à nouveau pour donner Gc et Gg. Mais ces trois allèles coexistent dans l'espèce. Puis Il y a séparation en 2 espèces B et G, l'espèce G possède après quelques générations seulement l'allèle Gg (Il y a eu par hasard disparition de certains allèles. C'est le tri de lignage incomplet.) Puis l'espèce B se sépare en espèce H et C. L'espèce H possède après quelques générations uniquement l'allèle Gh et l'espèce C uniquement l'allèle Gc. Mais ce gène n'est pas à l'origine de la spéciation. Il dérive juste au hasard. Si on utilise le gène G pour faire un arbre phylogénétique, on aura l'impression que les espèces G et C ont divergé ensemble en premier, puis seulement après l'espèce H. Si on utilise des gènes à l'origine de la spéciation ou ayant divergé après, on obtiendra un autre arbre phylogénétique(cladogramme) qui correspondra plus à la réalité. Le tri de lignage incomplet est donc à l'origine d'arbres discordants.
Dans le cas de tri de lignage complet tout les allèles persistent dans les espèces filles.
L'arbre produit par un seul gène diffère de l'arbre au niveau de la population ou de l'espèce, produisant un arbre discordant. En conséquence, un arbre généré au niveau de l'espèce peut différer en fonction des gènes sélectionnés utilisés pour l'évaluation, contrairement au tri de lignées complet, où l'arbre produit par le gène est le même que l'arbre au niveau de la population ou de l'espèce. Ces deux types de résultats sont courants en analyse phylogénétique, bien que cela dépende du gène, de l'organisme et de la technique d'échantillonnage.
Notes et références
- ↑ Michael G Simpson, Plant Systematics, , 752 p. (ISBN 978-0-08-092208-9, lire en ligne)
- ↑ A Kuritzin, T Kischka, J Schmitz et G Churakov, « Incomplete Lineage Sorting and Hybridization Statistics for Large-Scale Retroposon Insertion Data », PLOS Computational Biology, vol. 12, no 3, , e1004812 (PMID 26967525, PMCID 4788455, DOI 10.1371/journal.pcbi.1004812, Bibcode 2016PLSCB..12E4812K)
- ↑ A Suh, L Smeds et H Ellegren, « The Dynamics of Incomplete Lineage Sorting across the Ancient Adaptive Radiation of Neoavian Birds », PLOS Biology, vol. 13, no 8, , e1002224 (PMID 26284513, PMCID 4540587, DOI 10.1371/journal.pbio.1002224)
- ↑ Magali Semeria. Évolution de l’architecture des génomes : modélisation et reconstruction phylogénétique. Génétique. Université Claude Bernard - Lyon I, 2015.
- Portail de la biologie
- Portail origine et évolution du vivant